Материал: Потапов В.В. Решение задач биоинформатики при помощи веб - и интернет-сервисов
3.Когда вы выберите все интересующие вас последовательности чтобы построить филогенетическое древо щелкните внизу на кнопку «Множественное выравнивание».
Так вы сможете воспользоваться сервисом который выравнивает заданный набор последовательностей, то есть расставляет гэпы так чтобы похожие участки в разных последовательностях находились одни под другим.
Для выполнения выравнивания нажмите на кнопку «рассчитать» с теми последовательностями во входной форме, которые туда были внесены когда вы перешли со страницы с результатами скрининга.;
4.После того как последовательности будут выровнены, щелкните внизу страницы с результатом выравнивания на ссылку «Перейти к филогенетическому анализу»
5.Через встроенную на сайте систему автоматических переходов (которые по английски называются pipelines) сформированный вами запрос перенаправляется на сервис Филогенетический анализ, здесь вы можете выбрать метод анализа и скомандовать «Рассчитать».
6.Результат построения филогенетического древа появляется практически мгновенно и вы сможете оценить эволюционные расстояния внутри выбранной вами группы вирусов и топологию построенного дерева.
5.2.4Конструирование трехмерной структуры вирусного белка NS3
Все задания выполненные до этого момента, были некоторым экскурсом для знакомства с исследуемым нами объектом, а теперь нам предстоит захватывающий этап работы, называемый Insight into, то есть взгляд внутрь. Давайте немного поразмышляем, над нашим объектом и устройством всего живого в целом. Из специализированных баз данных мы можем извлечь генетические последовательности практически для всех живых организмов живущих на Земле. Но что из себя представляет сама последовательность с точки зрения живой природы? Это - определенная матрица с которой синтезируется множество белков, выполняющих свои особенные исключительные функции в живом
36
организме. А благодаря белкам и существует живая материя. Как по настоящему выглядят белки, белки из которых состоит наше тело, или белки вирусной частицы, или любые другие белки? Для того чтобы узнать как выглядят белки в живой природе, существует несколько достаточно сложных экспериментальных методов - получение кристаллов белка и расшифровка их структуры с помощью рентгеноструктурного анализа и метод ядерно-магнитного резонанса, а так же компьютерное молекулярное моделирование.
Метод компьютерного молекулярного моделирования, в отличии от экспериментальных методов, позволяет получать лишь предсказания структуры белков, и эти предсказанные структуры могут отличаться от экспериментально наблюдаемых. По сути они представляют собой результаты эксперимента, который выполняется in silico, то есть на компьютере. Именно поэтому на сегодняшний день с помощью моделирования можно получить пространственную структуру белка достаточно быстро и дешево, хотя без дополнительной верификации такая структура будет отличаться от реального белка в растворе. В зависимости от требований к точности пространственной структуры выбираются разные методы либо долгие и дорогостоящие исследования с кристаллизацией белка, либо быстрые и малозатратные компьютерные эксперименты.
У нас есть последовательность вирусного белка NS3 по которой мы хотим воссоздать его третичную структуру, то есть увидеть как этот белок выглядит в природе.
Для этого воспользуемся известным методом моделирования по гомологии, этот метод также называется гомологичное моделирование, либо сравнительное моделирование.
Вкратце, суть метода можно описать так: существует база данных экспериментально определенных структур белков. Мы собираемся найти в этой базе структуру белка, который имеет гомологию по первичной последовательности с нашим заданным белком, и на основании найденной гомологии построить трехмерную модель нашего белка.
Несмотря на то что в базе данных PDB хранится огромное множество трехмерных моделей для самых разных белков, не всегда можно найти расшифрованную пространственную структуру непосредственно интересующего вас белка. Например, для исследуемого белка NS3 вируса клещевого энцефалита в PDB в настоящее время нет ни одной структуры. Однако если продолжить поиск в базе PDB можно найти
37

структуры этого же белка для близкородственных видов вируса того же рода и семейства. Если в базе белковых структур мы нашли хотя бы одну модель близкородственного белка, то можно приступать к моделированию по гомологии. Для выполнения задания по конструированию пространственной структуры вирусного белка NS3 воспользуемся сервисом «скрининг по гомологии (PDB)» на www.brishur.com
1.Откройте страницу сервиса Скрининг по гомологии (PDB)
2.По аналогии с предыдущими запросами заполните поля email и наименование задания Возьмите исследуемую последовательность белка NS3 и вставьте в поле «Последовательность»
3.Для уменьшения времени расчетов воспользуемся параметрами, заданными по умолчанию:
4.Метод скрининга для построения профиля Genebee
5.Количество последовательностей в полученном результате 100.
6.Cкомандуем «Рассчитать».
Рисунок 17: Bri-shur - скрининг по гомологии (PDB)
38

7.После выполнения задания в полученном вами письме перейдите по ссылке на страницу с результатом вашего запроса.
8.На странице со списком найденных гомологов выберите элемент списка с наибольшим значением Z-score
9.Щелкните внизу страницы на кнопку «Уточнить парное выравнивание»
10.Через систему пайплайнов вы окажетесь на сервисе множественное выравнивание.
11.Cкомандуем «Рассчитать».
12.Посмотрите на результат выравнивания и зрительно оцените процент сходства и совпадения исследуемой и найденной последовательностей, ориентируясь на количество условных символов * или +
13.Внизу страницы перейдите по ссылке «Перейти к моделированию по гомологии»
Рисунок 18: Bri-shur - задание параметров моделирования по гомологии в Nest
14.На странице «Nest (Гомологичное моделирование)» можно еще раз посмотреть выравнивание, щелкнув по кнопке «Предварительный просмотр выравнивания»
39
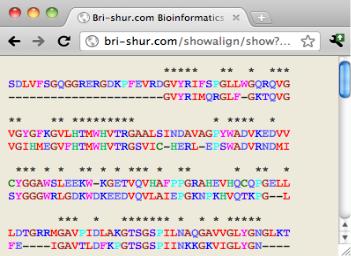
Рисунок 19: Bri-shur - пример выровненных последовательностей
15.Скомандуем «Рассчитать».
16.Через минуту обновите страницу и если задание выполнено щелкните на ссылку download и загрузите готовую трехмерную модель структуры белка в формате файла pdb на свой компьютер.
17.Далее визуализируйте модель с помощью программы Chimera, описанной выше.
40